近日,计算机科学顶级期刊、中国科学院SCI一区Top期刊、CCF B类期刊《Pattern Recognition》发表了计算机与大数据科学学院生物信息团队关于cicrRNA-disease关联预测方法最新研究进展。论文题目为“Multiple similarity and multiple kernel fusion based on graph inference network for circRNA-disease association prediction”(《基于图推理网络的多相似性与多核融合环状RNA-疾病关联预测》)。九江学院为论文的第一署名单位,计算机与大数据科学学院李先彬博士为论文第一作者兼通讯作者,合作者包括计算机与大数据科学学院刘涛副教授、汪彬彬博士、药生学院曾明博士,青海理工学院张顺利副教授。
环状RNA(circRNAs)是疾病发生的关键调控因子,其与疾病的关联预测对理解致病机制具有重要意义。然而,现有计算方法仍面临相似性网络信息利用不足、关联数据缺失以及多源信息整合效率低等挑战。为此,李先彬博士所在的生物信息团队提出一种基于图推理网络的多相似度与多核融合模型(MMGINCDA)。该模型首先通过相似度矩阵融合技术,动态整合环状RNA与疾病的多类相似性信息,并引入已知关联以自适应增强拓扑表征。其次,采用截断反正切秩最小化对关联矩阵进行补全,提升网络结构的稳健性。最后,通过图推理网络协同利用局部与全局相似性,同时抑制远端节点干扰。实验表明,MMGINCDA在多个基准数据集上均优于现有主流方法。消融实验与案例分析进一步验证了模型在预测潜在环状RNA-疾病关联方面的准确性与实用性。本研究为环状RNA相关疾病机制的研究提供了可靠的计算框架。
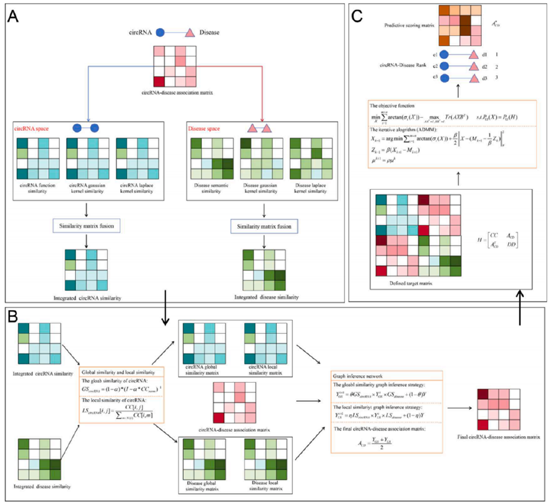
方法流程图
李先彬博士所在的生物信息团队近年来一直致力于生物信息方向研究,包括药物重定位预测方法、药物靶点预测、miRNA-疾病、circRNA-疾病关联关系预测等应用,取得了很多研究成果。
该研究得到了国家自然科学基金项目的支持。
论文链接:https://www.sciencedirect.com/science/article/pii/S0031320326004322,DOI: 10.1016/j.patcog.2026.113466
李先彬供稿
责编:魏东平 审核:彭虎 董西伟